Cuando un niño presentaba síntomas como fiebre alta, dolor de garganta y un áspero sarpullido rojo, los diagnósticos que se planteaban eran la viruela, el sarampión o la difteria. Sin embargo, el descubrimiento a finales del siglo XIX de la bacteria Streptococcus pyogenes introdujo una nueva enfermedad: la escarlatina.
La escarlatina era una de las principales causas de muerte y discapacidad infantil, puesto que con frecuencia provocaba pérdida de visión y audición. Con el desarrollo de los antibióticos, la fiebre escarlata se ha convertido en una infección bacteriana tratable y con un pronóstico muy favorable.
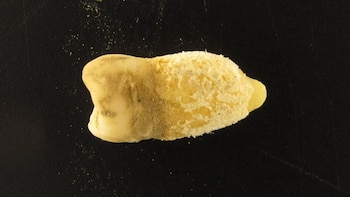
La historia de la medicina narraba que esta infección fue llevada por los europeos a América en tiempos de la colonización. Sin embargo, el diente de una momia precolombina podría cambiar lo que creíamos saber sobre la escarlatina. Así lo revela un estudio recién publicado en la revista Nature Communications.
Tras analizar el ADN de una pieza dental de un hombre momificado que vivió entre 1283 y 1383 d.C. en la actual Bolivia, un equipo de científicos del Instituto de Estudios de Momias de Eurac ha descubierto restos de la infección bacteriana. Esto significaría que el patógeno ya circulaba entre las poblaciones indígenas siglos antes de la llegada de los europeos a América.
“La cepa antigua portaba muchos, aunque no todos, de los genes patógenos que se encuentran en las cepas modernas de Streptococcus pyogenes“, explica el microbiólogo Frank Maixner, director del Instituto de Estudios de Momias de Eurac. Esta cepa antigua parece estar estrechamente relacionada con las modernas, de las que podría haberse separado hace 10.000 años y que hoy en día provocan infecciones de garganta.
Un patógeno que circula desde hace 4.000 años
La evidencia científica disponible apunta a que los primeros pobladores de América cruzaron el estrecho de Bering hace unos 22.000 años. Paralelamente, datos genómicos sugieren ahora que Streptococcus pyogenes ya circulaba en Europa y África hace al menos 4.000 años. Este escenario abre la posibilidad de que los seres humanos hayan convivido durante milenios con esta bacteria, con Siberia como posible punto de entrada para su expansión hacia otros territorios.
“La presencia de S. pyogenes en distintas regiones geográficas y periodos de tiempo plantea la posibilidad de que fuera transportada por las poblaciones humanas durante sus migraciones, contribuyendo así a su distribución global”, especulan los autores del estudio.
Tradicionalmente, estas patologías han sido consideradas “enfermedades de la frontera”, asociadas a la llegada de colonos europeos al continente americano y al impacto devastador que tuvieron sobre poblaciones con sistemas inmunitarios menos preparados. No obstante, esta interpretación podría resultar excesivamente simplista, también en el caso de la escarlatina.
Otras investigaciones recientes basadas en ADN antiguo hallado en Colombia plantean que la sífilis pudo haber existido tanto en América como en Europa durante miles de años, lo que cuestiona la idea de que su propagación inicial estuviera ligada exclusivamente al contacto con poblaciones americanas. Un patrón similar se observa en enfermedades como la lepra y, posiblemente, también en la escarlatina.
Una momia boliviana para reescribir la historia
En este contexto, los fragmentos de ADN antiguo de S. pyogenes recuperados de un diente perteneciente a una momia boliviana se encuentran altamente degradados. A pesar de ello, los investigadores lograron extraer información suficiente para reconstruir parcialmente su genoma.
“Se puede pensar en ello como armar un rompecabezas sin conocer la imagen de la caja”, explica el microbiólogo Mohamed Sarhan de Eurac. El proceso, aunque complejo, presenta ventajas metodológicas. Según Sarhan, “no se dejan influenciar por referencias modernas”, puesto que trabajan “sin ideas preconcebidas”. “Esto nos permite descubrir perspectivas totalmente nuevas e identificar variantes genéticas que quizás ya no existan”, asegura.
Hasta ahora, en estudios de ADN antiguo, las secuencias más largas solían descartarse al considerarse posibles contaminaciones modernas, bajo la premisa de que no podían haberse conservado durante tanto tiempo. Sin embargo, la nueva investigación cuestiona este supuesto. Según el investigador Maixner, este hallazgo “pone en tela de juicio los fundamentos de la investigación del ADN antiguo”.
Últimas Noticias
Tres de cada cuatro españoles creen que los propietarios de varias viviendas deberían pagar más impuestos
Un 72% respalda restringir la compra de vivienda para inversión, el 68% apoya limitar el precio de los alquileres en su zona y un 82,9% pide aumentar la inversión pública en vivienda asequible

La Audiencia Nacional rechaza el asilo a un saharaui que alegó que Marruecos no quería atender a su hijo con una enfermedad grave
El tribunal señala que el derecho a la protección internacional no puede utilizarse como vía para mejorar las condiciones de vida o acceder a servicios sanitarios de mayor calidad en otro país

Otitis: causas, síntomas y tratamiento de esta infección de oído
El dolor de oído, la secreción de líquido o el enrojecimiento del canal auditivo son algunos de sus síntomas
Este es el precio de la gasolina en Madrid, Barcelona y otras ciudades de España este 21 de abril
El valor de los combustibles cambia todos los días, por eso es importante mantenerse informado sobre su valor

De Fabiana Sevillano a Eugenia Osborne: los mejores looks de las famosas en el Pescaíto de la Feria de Sevilla
La primera noche de la Feria de Abril ha dejado infinidad de estilismos que marcan una clara tendencia: colores neutros, mantones de Manila y chaquetas toreras



