
A seis meses del comienzo de la pandemia de COVID-19, con más de 5 millones de infectados en el mundo y casi 340.000 muertos, la búsqueda de un tratamiento contra el nuevo coronavirus es tan urgente como la de una vacuna. Pero al igual que el proceso de desarrollo de una vacuna lleva cinco años —distintos esfuerzos internacionales intentan acortarlo a 18 meses en esta emergencia sanitaria global—, el de un antiviral requiere tiempo. Y mucho: desde la concepción de una droga nueva hasta su llegada al mercado suelen pasar 12 años en promedio.
“Necesitamos con urgencia drogas efectivas, pero ¿cuál es la manera más rápida de hallarlas?”, plantearon Jerry Parks, del Laboratorio Nacional de Oak Ridge, y Jeremy Smith, del Departamento de Bioquímica y Biología Molecular, ambos de la Universidad de Tennessee, Estados Unidos. “Un enfoque que en ocasiones se parece a un pase largo del fútbol americano, es tener la esperanza de que drogas que han funcionado contra otros virus (como los de la hepatitis C o el ébola) también funcionarán contra el COVID-19”.
PUBLICIDAD
En el pase largo o bomba, que en México se conoce como “Ave María Dame Puntería”, se utiliza en los últimos minutos de un partido, cuando una formación de cinco jugadores corre a toda velocidad hacia la zona de anotación mientras el mariscal de campo arroja la pelota a ciegas y por si alguno tiene la posibilidad de atraparla.
Pero también hay otra posibilidad, que surgió en las décadas de 1950 y 1960 cuando —por entonces, con la ayuda de cristalografía de rayos X— se pensó en emplear información de las estructuras de las proteínas para guiar el diseño de drogas nuevas. El acceso a estructuras tridimensionales de proteínas importantes para las terapias permitió identificar puntos potenciales de inhibición, lo cual dio base al diseño de fármacos basado en ellas, que desde la década de 1980 tuvo un gran desarrollo dada la gran evolución de la biotecnología. Y que actualmente, gracias al poder de cálculo sin precedentes de las máquinas, ha dado origen al diseño de fármacos asistido por computadora (DIFAC).
PUBLICIDAD
A eso apuntan Parks y Smith: “Podemos ser racionales y dirigirnos específicamente a las proteínas del SARS-CoV-2 para interrumpir su ciclo vital”, propusieron en The New England Journal of Medicine (NEJM), en lugar de la práctica improbable del pase largo.
“Los adelantos veloces en química combinatoria y tecnologías de cribado químico ultrarrápido han creado un entorno para acelerar el proceso del descubrimiento de medicamentos al permitir que se seleccionen y se sinteticen, en poco tiempo, bibliotecas enteras de compuestos", describieron. Eso es una ventaja fundamental en un campo que exige enormes inversiones: además del periodo de 12 años, en promedio se gasta USD 1.000 millones por el diseño de una droga nueva. Y aun así el camino está plagado del riesgo de baja eficacia e incluso de fracaso.
PUBLICIDAD

“En consecuencia, se han desarrollado enfoques diferentes para abreviar el ciclo de investigación y reducir los costos y el riesgo de fracaso en el descubrimiento de medicamentos”, agregaron. “El DIFAC es uno de los métodos más eficaces para alcanzar estos objetivos”.
El nuevo coronavirus, cuyo genoma fue decodificado en enero, contiene unas 25 proteínas que le son útiles para infectar a los seres humanos, en primer lugar, y replicarse luego. La más conocida es la proteína de punta, lo que parecen espinas del virus (y le dan el nombre de corona) que se pega a una proteína de superficie de las células humanas llamada enzima convertidora de angiotensina (ECA), en la etapa inicial de la infección. Los bioquímicos enumeraron también la ARN polimerasa, que sintetiza el material genético del virus, y la endonucleasa que realiza la segmentación del material genético, es decir que comienza las divisiones para que el virus se multiplique.
PUBLICIDAD
Cualquiera de ellas es un buen blanco: “Hallar medicamentos que puedan unirse a las proteínas virales y evitar que funcionen es una forma lógica de avanzar, y la prioridad de muchos laboratorios de investigación”, escribieron Parks y Smith.
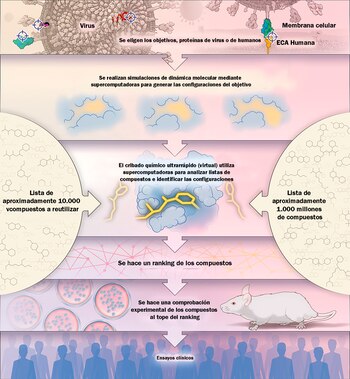
Entre ellos el Laboratorio Nacional de Oak Ridge, que utilizó la máquina más poderosa e inteligente del mundo, llamada Summit, para identificar (hasta ahora) 77 compuestos moleculares de drogas que podrían llega a presentar una esperanza contra el COVID-19, y justificar estudios más profundos, según contó Smith al periódico de esa localidad de Tennessee.
PUBLICIDAD
“Con la supercomputadora podemos hacer en un día los cálculos que en un ordenador común nos llevarían un mes", agregó Smith sobre la cantidad de variaciones posibles a la hora de probar combinaciones que pudieran ser eficaces contra el virus. “En este mismo instante la supercomputadora hace cálculos para tratar de obtener una estimación más afinada de cuáles compuestos podrían funcionar”, agregó a la radio de Huntsville.
Una de las maneras en que proceden esos cálculos es la imitación de la naturaleza. En modelos tridimensionales de las proteínas que son los objetivos, Summit junta los compuestos en los puntos de unión potenciales. Para establecer si son afines, más o menos afines, o no lo son en absoluto, se recurre a ecuaciones basadas en la física que otorgan un valor numérico a las interacciones entre el compuesto y la proteína. Los que encabezan el ranking, y no la enorme cantidad originalmente posible, pasan a experimentos para comprobar si efectivamente se unen y logran detener la infección viral en células humanas y en animales.
PUBLICIDAD

Cuando se comenzaron a poner en práctica estos métodos sofisticados —en la década de 1990, cuando otra pandemia sacudía al mundo: el VIH— el proceso resultó poco eficiente: “Las computadoras eran tan débiles que sólo se podían acoplar unos 100 compuestos a la vez”, escribieron Parks y Smith. Hoy ellos trabajan con unos 10.000 de una lista de 1.000 millones.
Gracias a la potencia de las actuales máquinas como Summit, el cribado químico ultrarrápido virtual (el proceso de tamizaje de los elementos que selecciona los que tienen potencial y los que no) “puede identificar rápidamente compuestos que se unen con fuerza”. A diferencia de las simulaciones que se hacían a fines del siglo XX, hoy se toman en cuenta para los cálculos factores como los movimientos internos de las proteínas, lo cual permite ver más opciones que en el pasado.
PUBLICIDAD

Summit realiza procesamientos masivos de manera simultánea, lo cual “permite que las simulaciones de la dinámica molecular de muchas réplicas del objetivo se ejecuten en paralelo”, es decir que se consideren distintas opciones al mismo tiempo. “Con el uso de Summit, en un día se puede obtener un modelo de simulación completo de un objetivo para una droga contra el SARS-CoV-2 basada en proteínas, mientras que con el uso de un típico conglomerado de computadoras se tardaría meses”, escribieron los expertos. “De esta manera, el campo del DIFAC está preparado para obtener resultados rápidos”.
Parks y Smith publicaron antes, en febrero, sus primeros resultados: el procesamiento de unos 8.000 compuestos que potencialmente se unen a la proteína de punta del SARS-CoV-2 a fin de inhabilitarlo, y en la actualidad realizan pruebas sobre el virus vivo con los que clasificaron mejor entonces.
PUBLICIDAD
MÁS SOBRE ESTE TEMA:
PUBLICIDAD
PUBLICIDAD
Últimas Noticias
Cómo las gotas de agua explotan al evaporarse y por qué ese hallazgo podría cambiar la nanotecnología
La fisión de Coulomb, una predicción formulada en 1882 y confirmada ahora en superficies sin fricción, abre camino hacia técnicas de electrospray más eficientes y sustentables, sin necesidad de alto voltaje

Qué dicen los expertos sobre los documentos ovni que Estados Unidos hizo públicos: “Fenómenos imposibles de explicar”
La presidenta de CEFORA, Andrea Pérez Simondini, analizó en Infobae a la Tarde el material desclasificado por el Pentágono y explicó por qué la ciencia aún no logra identificar el origen de los objetos reportados por pilotos y radares militares

Afirman que un asteroide “decapitado” dio origen al mayor cráter en la Luna
Astrónomos simularon un nuevo modelo que sugiere que la cuenca Polo Sur-Aitken fue producto de un impacto único. Una misión Artemis podría recuperar fragmentos del manto lunar

La llegada de un Super Niño preocupa a la región por una posible alteración climática
Modelos globales meteorológicos de Estados Unidos y Europa anticipan un fenómeno extremo para el último trimestre de 2026. Las anomalías oceánicas podrían afectar especialmente a la agricultura y el caudal hídrico

Cómo es el ratón colilargo que puede transmitir el hantavirus Andes
Se trata de un pequeño roedor silvestre que habita los bosques andino-patagónicos de Argentina y Chile. Su presencia forma parte del equilibrio natural del ecosistema, sin intención ni culpa en la transmisión del patógeno




